核酸的折叠热力学可以用自由能变、焓变和熵变等参数定量描述,这对于表征核酸结构的稳定性和功能性至关重要。预测和测量基于经典碱基配对规则的DNA结构的热力学特性相对容易,但对于在生物学功能和生物技术应用上同样十分重要的非经典核酸(G-四链体、三链体和i-基序等)而言,直接测量其在原位环境下的热力学仍然具有挑战性。
我院李峰教授课题组基于可编程的动态 DNA 化学,开发了自由能迁移分析 (FESA)工具,成功实现了非经典核酸折叠热力学参数的原位表征。相较于传统的DNA热力学测量方法(DNA熔解或滴定),它具有以下主要优势:(1)FESA 提供自由能转移的直接测量,不依赖于数学假设或近似,从而确保结果的可靠性。(2)它允许在原位条件下表征核酸结构,无需不断调整温度和反应物比等实验参数,可在各种温度、pH 水平和金属离子浓度下有效运行。(3)FESA 灵敏度高,可以在低纳摩尔浓度范围内测量微小的热力学变化。(4)FESA 不需要专门的仪器,因此任何具有基本台式设施的生化实验室都可以使用。FESA 的成功开发标志着通过分子工具表征非规范 DNA 结构热力学的技术进步,开辟了从分子工程和动态 DNA 化学视角探究基本化学和生物物理问题的新途径。
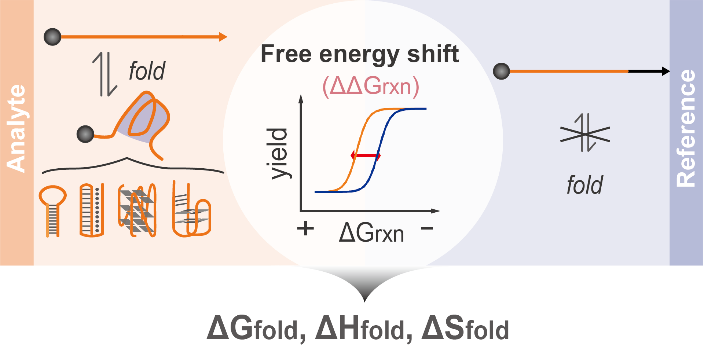
图1.FESA的原理示意图
该工作于2024年6月发表于Journal of the American Chemical Society期刊,题目为“Native characterization of noncanonical nucleic acid thermodynamics via programmable dynamic DNA chemistry”。澳门新莆京游戏大厅为第一单位,李峰教授为通讯作者,澳门新莆京游戏大厅博士研究生吴宇琴和专职博士后王冠为共同第一作者。
文章链接:https://doi.org/10.1021/jacs.4c04721
